WnioskowanieStatystyczne/Elementy statystyki wielowymiarowej
Spis treści
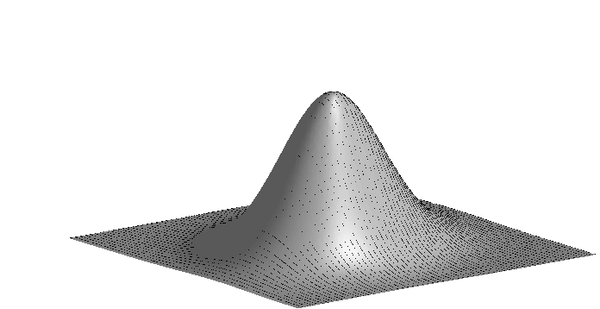
Dwumianowy rozkład normalny
[math] f(t)=ke^{-\frac{1}{2}(t-\mu )A(t-\mu )^{T}} [/math]
[math]t=(x,y)-[/math] wektor zmiennej losowej
[math]\mu =(\mu _{1},\mu _{2})-[/math] wektor wartości oczekiwanych
[math]k-[/math] stała normalizjąca
[math]A-[/math] odwrotność macierzy kowariancji [math]C[/math]
[math] A=\left[ \begin{matrix} \sigma _{x}^{2} & \sigma _{xy} \\ \sigma _{xy} & \sigma _{y}^{2} \end{matrix} \right] ^{-1}=\frac{1}{\sigma _{x}^{2}\sigma _{y}^{2}-\left( \sigma _{xy}\right) ^{2}}\left[ \begin{matrix} \sigma _{y}^{2} & -\sigma _{xy} \\ -\sigma _{xy} & \sigma _{x}^{2} \end{matrix} \right] [/math]
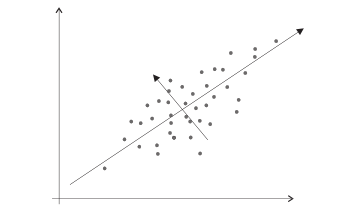
Macierz kowariancji
dla [math]x=(x_{1,}x_{2})[/math] i [math]\mu =(\mu _{1}, \mu _{2})[/math]
[math]\begin{matrix} C=E\left[ \left(\begin{matrix}{x_{1}-\mu _{1}}\\ {x_{2}-\mu _{2}} \end{matrix} \right) \left( x_{1}-\mu_{1},x_{2}-\mu _{2}\right) \right] =\left[ \begin{matrix} E\left[ \left( x_{1}-\mu _{1}\right) ^{2}\right] & E\left[ \left( x_{1}-\mu _{1}\right) \left( x_{2}-\mu _{2}\right) \right] \\ E\left[ \left( x_{2}-\mu _{2}\right) \left( x_{1}-\mu _{1}\right) \right] & E \left[ \left( x_{2}-\mu _{2}\right) ^{2}\right] \end{matrix} \right] = \\ \left[ \begin{matrix} \sigma _{1}^{2} & \sigma _{12} \\ \sigma _{21} & \sigma _{2}^{2} \end{matrix} \right] \end{matrix} [/math]
Interpretacja współczynnika korelacji znajduje się pod hasłem Regresja liniowa.
Analiza wariancji wielu zmiennych (Multivariate ANalysis of VAriance — MANOVA)
Zmienna losowa [math]X[/math] opisywana wektorem ([math]x_{1},...,x_{k})[/math], podobnie wartość średnia staje się wektorem o tym samym wymiarze: ([math] \mu _{1},...,\mu _{k}).[/math] Macierz kowariancji (%i 1) zmiennej losowej
[math] S=\left[ \begin{matrix} \upsilon ar(x_{1}) & co\upsilon (x_{1},x_{2}) & ... & co\upsilon (x_{1},x_{k}) \\ co\upsilon (x_{2},x_{1}) & \upsilon ar(x_{2}) & ... & co\upsilon (x_{2},x_{k}) \\ ... & ... & ... & ... \\ co\upsilon \left( x_{k},x_{1}\right) & co\upsilon (x_{k},x_{2}) & ... & \upsilon ar(x_{k}) \end{matrix} \right] [/math]
gdzie:
[math] \upsilon ar(x_{i})=\sigma _{x_{i}}=E((x_{i}-\mu _{i})^{2}) [/math]
[math] co\upsilon (x_{i},x_{k})=\sigma _{x_{i},x_{k}}=E((x_{i}-\mu _{i})(x_{k}-\mu _{k})) [/math]
Wielowymiarowy rozkład normalny
[math] \Phi (X)=\frac{1}{\sqrt{(2\pi )^{k}}\sqrt{\left| S\right| }}e^{-\frac{(X-\mu )^{\prime }S^{-1}(X-\mu )}{2}} [/math]
Od tego momentu przyjmujemy, że zmienne [math]X[/math] podlegają takiemu właśnie rozkładowi. Jeśli [math]X[/math] pochodzą z próby podzielonej na grupy, to podobnie jak w [math]ANOVA[/math] możemy skonstruować macierze wariancji wewnątrzgrupowych i międzygrupowych i dowieść, że [math]S=S_{wew}+S_{pom}[/math]. Iloraz wyznaczników macierzy [math]S_{wew}[/math] i [math]S[/math] podlega rozkładowi [math]\Lambda [/math] Wilksa:
[math] \Lambda =\frac{\left| S_{wew}\right| }{\left| S\right| }=\frac{\left| S_{wew}\right| }{\left| S_{wew}+S_{pom}\right| } [/math]
i służy testowaniu hipotezy o braku różnic między grupami. Ogólnie statystyki Wilksa można używać do testowania hipotezy [math]h[/math] w postaci
[math] \Lambda =\frac{\left| S_{wew}\right| }{\left| S_{wew}+S_{h}\right| } [/math]
gdzie [math]S_{h}[/math] — macierz kowariancji odpowiadająca testowanej hipotezie.
Niektóre z pominiętych haseł — w skrócie
Analiza składowych głównych (Principal Components Analysis, PCA)
Przedstawiamy macierz kowariancji w postaci diagonalnej
[math] S=\left[ \begin{matrix} r_{11} & r_{12} & ... & r_{1k} \\ r_{21} & r_{22} & ... & r_{2k} \\ ... & ... & ... & ... \\ r_{k1} & r_{k2} & ... & r_{kk} \end{matrix} \right] \left[ \begin{matrix} \lambda _{1} & 0 & ... & 0 \\ 0 & \lambda _{2} & ... & 0 \\ ... & ... & ... & ... \\ 0 & 0 & ... & \lambda _{k} \end{matrix} \right] \left[ \begin{matrix} r_{11} & r_{21} & ... & r_{k1} \\ r_{12} & r_{22} & ... & r_{k2} \\ ... & ... & ... & ... \\ r_{1k} & r_{2k} & ... & r_{kk} \end{matrix} \right] [/math]
Wielkości [math]\lambda _{i}[/math] są rozwiązaniami równania [math]\left| S-\lambda I\right| =0,[/math] a wektor [math]r_{i}[/math] osiami nowego układu współrzędnych. Składowe [math]PCA[/math] są liniowymi kombinacjami obserwowanych zmiennych.
Analiza dyskryminacyjna (Discriminant Analysis )
Wielowymiarowe wektory próby [math]X[/math] mamy podzielone na grupy, szukamy funkcji najlepiej je rozdzielającej, która umożliwi zaklasyfikowanie nowej obserwacji. Rozdzielenie grup odpowiada w przypadku jednowymiarowym maksymalizacji stosunku wariancji międzygrupowej do wariancji wewnątrzgrupowej
[math] F=\frac{\left( n-k\right) s_{pom}}{\left( k-1\right) s_{wew}} [/math]
W przypadku wielowymiarowym mamy do czynienia z macierzami kowariancji; możemy rozpatrywać wielkość
[math] F_{a}=\frac{a^{\prime }S_{pom}a}{a^{\prime }S_{wew}a} [/math]
Maksymalizacja tej wielkości względem [math]a[/math] daje wektor własny macierzy [math]S_{wew}^{-1}S_{pom}[/math] odpowiadający największej wartości własnej. Wektory własne odpowiadające kolejnym wartościom własnym zwiemy współrzędnymi dyskryminacyjnymi, tworzącymi przestrzeń dyskryminacyjną.
Analiza czynnikowa (Factor Analysis )
opiera się na założeniu istnienia ukrytych czynników, stara się przedstawić obserwowane zmienne w postaci:
obserwowana zmienna = liniowa kombinacja czynników + błąd
w odróżnieniu od PCA, realizującej model
składowa = liniowa kombinacja obserwowanych zmiennych
Analiza skupień — Cluster Analysis
Wejściem dla tej procedury jest zestaw danych, a wyjściem ich podział na grupy. Można go zrealizować na wiele sposobów: [math]N[/math] punktów [math]x^{1}...x^{N},[/math] z których każdy opisany jest przez [math]k[/math] cech [math]x_{1}...x_{k}[/math].
Metody polegające na kolejnym łączeniu punktów
Startujemy z N klastrów jednopunktowych, w każdym kroku łączymy najbliższe. Wynikiem działania jest drzewo łączenia, na którym sami musimy wybrać ilość klastrów. Wynik zależy silnie od przyjętych definicji odległości między klastrami oraz definicji odległości między punktami.
Odległości między punktami:
- Odległość Euklidesowa [math]d(x,y)=\sqrt{\underset{i=1}{\overset{k}{\sum }}(x_{i}-y_{i})^{2}}[/math] (czuła na różne skale cech).
- Odległość korelacyjna [math]d(x,y)=1-\rho (x,y),[/math] gdzie [math]\rho (x,y)=\frac{\underset{i=1}{\overset{k}{\sum }}(x-\overline{x})(y- \overline{y})}{\sigma _{x}\sigma _{y}} [/math] (znormalizowana do przedziału (0,2), mniejsza im lepiej skorelowane punkty).
Odległości między klastrami:
- Najbliższego sąsiada (single linkage) - odległość między dwoma najbliższymi elementami klastrów [math]A[/math] i [math]B[/math]: [math]d(A,B)=\min_{x,y}d(x,y),\ \ \ \ \ x\in A,\ y\in B[/math]
- (complete linkage ) - odległość między dwoma najbliższymi elementami klastrów [math]A[/math] i [math]B[/math]: [math]d(A,B)=\max_{x,y}d(x,y),\ \ \ \ \ x\in A,\ y\in B [/math]
- (centroid) - odległość między środkami klastrów,
- (avarage) - średnia odległości, itd...
Metoda K–średnich (K – means )
Wybieramy ilość klastrów, podział dokonywany jest w iteracyjnej procedurze dążącej do minimalizacji stosunku wariancji pomiędzy klastrami do wariancji wewnątrz klastrów - niejako [math]ANOVA[/math] bez ustalonego wstępnie przyporządkowania, maksimum [math] F[/math] poszukiwane drogą przemieszczania elementów między klastrami.